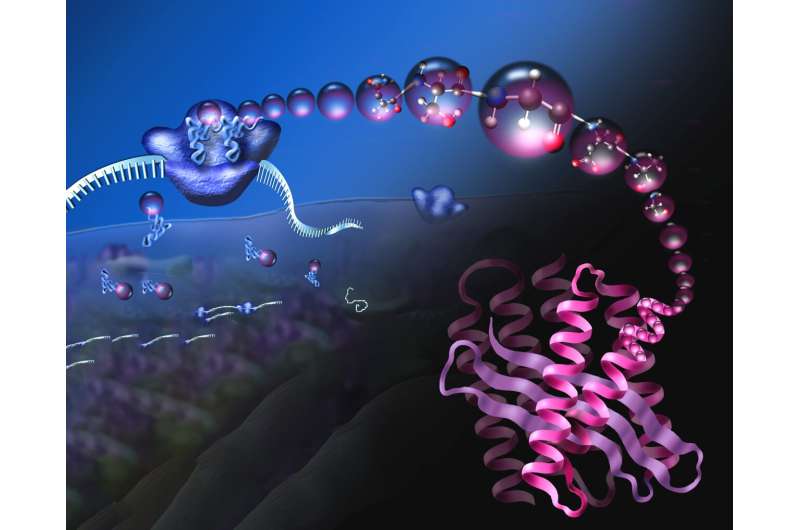
Ang mga ribosom (asul, sa ibabaw sa wala) mao ang mga nanomachines nga nagbasa sa mRNA (nga gikan sa wala) aron mag-assemble ug kadena sa mga amino acid (magenta balls) nga mapilo ngadto sa usa ka compact 3D protein (ubos nga tuo, pink). Credit: Gipahiangay gikan sa NSF
Ang mga sintetikong biologist nahimong mas mamugnaon sa engineering yeast o bacteria aron sa paghimog mapuslanong mga kemikal—gikan sa mga sugnod ngadto sa mga panapton ug mga droga—labaw pa sa normal nga repertoire sa mga mikrobyo.
Apan ang usa ka multi-unibersidad nga grupo sa mga chemist adunay mas ambisyoso nga tumong: ang pag-retool sa mga planta sa paggama sa polypeptide sa selula—ang mga ribosom nga nagtuyok sa mga amino acid ngadto sa protina—aron makamugna og mga polymer chain nga mas detalyado kay sa mahimo na karon sa usa ka cell o a test tube.
Ang panukiduki nga negosyo nga nakasentro sa Unibersidad sa California, Berkeley, karon nagreport sa hinungdanon nga pag-uswag sa kana nga katuyoan, ingon gipakita sa tulo ka bag-ong mga papel nga nag-atubang sa tulo ka dagkong mga babag: kung giunsa ang pag-reprogram sa mga selyula aron mahatagan ang ribosome sa mga bloke sa pagtukod gawas sa alpha-amino mga asido nga naglangkob sa tanang protina karon; kung giunsa pagtagna kung unsang mga bloke sa pagtukod ang naghimo sa labing kaayo nga substrate; ug kung giunsa pag-tweak ang ribosome aron maapil kini nga mga nobela nga mga bloke sa pagtukod sa mga polimer.
Ang katapusang tumong sa National Science Foundation Center for Genetically Encoded Materials (C-GEM) mao ang paghimo sa sistema sa paghubad nga hingpit nga maprograma, aron ang pagpaila sa mga instruksiyon sa mRNA ngadto sa selula uban sa bag-ong mga bloke sa pagtukod-dili ang alpha-amino acids nga makita karon— magtugot sa ribosome sa pagpatunghag walay kinutuban nga lainlain nga bag-ong mga kadena sa molekula. Kini nga mga kadena mahimong basehan alang sa bag-ong bio-material, bag-ong mga enzyme, bisan bag-ong mga tambal.
Ang mga papel, nga makita sa mga journal Kinaiyahan Chemistry ug ACS Central Sciencemao ang sinugdanan sa usa ka playbook alang sa reengineering sa cellular sintetikong makinarya aron makahimo sa wala pa makita nga mga polimer, lakip ang bio-polymers ug circular polymers, nga gitawag nga peptide macrocycles, nga adunay gitakda nga daan o hingpit nga wala damhang aplikasyon.
“Ang C-GEM nagtrabaho aron ma-biosynthesize ang mga molekula nga wala pa nahimo kaniadto sa usa ka selyula ug nga gidisenyo nga adunay talagsaon nga mga kabtangan. Ang mga himan mahimong magamit sa kadaghanan sa mga polymer chemist, mga chemist sa medisina ug mga biomaterial nga siyentipiko aron makamugna ang mga espesyal nga materyales nga adunay bag-ong mga gimbuhaton, “miingon ang direktor sa C-GEM nga si Alanna Schepartz, ang TZ ug Irmgard Chu Distinguished Chair sa Chemistry ug propesor sa molekular ug cell biology sa UC Berkeley. “Ang katapusang katuyoan mao ang pagpalapad sa function ug versatility sa mga protina ug polypeptides, ingon nga mga materyales ug mga parmasyutiko.”
Ang usa ka pananglitan, matod niya, mao ang pagprograma sa ribosome aron ma-synthesize ang usa ka polymer nga usa ka krus tali sa spider silk —usa sa labing gahi nga natural nga mga protina —ug naylon, usa ka polimer nga karon gihimo sa mga silid sa reaksyon sa kemikal. Samtang ang seda sa kaka mahimo na karon sa genetically engineered nga mga mikrobyo, ang teknolohiya nga C-GEM nga naugmad mahimong magtugot sa susamang mga mikrobyo sa paghimo sa usa ka walay kinutuban nga lainlain nga mga polimer nga nagsagol sa mga bloke sa pagtukod sa seda ug nylon, silang tanan bag-o sa mga chemist ug adunay talagsaon nga mga kabtangan. Ang teknolohiya mahimo usab nga gamiton sa paghimo sa mga polimer nga sama sa protina nga mas makasugakod sa kainit kay sa natural nga mga protina.
Ang usa ka gamhanan nga aspeto sa usa ka programmable ribosome machine nga makahimo sa pag-synthesize sa mga polymer mao nga kini nagtugot sa mga tigdukiduki sa pag-evolve sa mga polimer aron mahingpit ang ilang kalihokan, sama sa mga protina nga milambo sulod sa gatusan ka milyon nga mga tuig aron sa pagpalambo sa kalig-on sa mga selula ug mga organismo.
“Adunay kami mga polimer sa protina nga nag-uswag sa planeta sa bilyon-bilyon ka tuig, apan gipugngan kami kung unsa ang mga polimer tungod kay ang mga bloke sa pagtukod parehas nga 20 ka amino acid,” ingon ni Jamie Cate, propesor sa UC Berkeley sa chemistry ug sa molekular ug cell biology. “Kung makahimo kami usa ka sistema diin mahimo nimo nga magamit ang ebolusyon sa mga bag-ong polimer, nan kini sama sa usa ka plataporma nga magamit ni bisan kinsa nga adunay ideya sa paglalang aron mabag-o ang usa ka polimer sa usa ka butang nga gusto nila.”
Ang ingon nga sistema nagtukod sa gitumong nga ebolusyon sa mga enzyme sa protina diin si Frances Arnold, usa ka alumna sa UC Berkeley, nakadawat sa 2018 Nobel Prize sa Chemistry.
“Kini usa ka lakang nga labaw pa sa gibuhat ni Frances Arnold sa pagpalambo sa direksyon nga ebolusyon,” ingon ni Cate. “Gihimo niya ang gitumong nga ebolusyon alang sa mga protina. Ang among gipaningkamutan nga buhaton mao ang paghimo usa ka paagi nga mahimo nimo kini alang sa mga polimer nga wala pa kaniadto nausab sa kinaiyahan.”
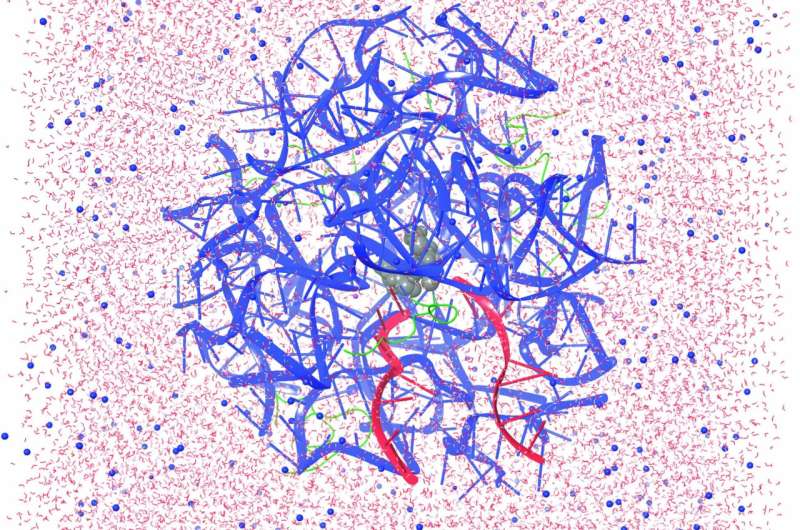
Ang mga tigdukiduki naghimo sa molecular dynamics simulations sa usa ka modelo nga sistema base sa cryo-EM nga mga pagtuon sa istruktura sa E. coli ribosome. Ang rehiyon sa ribosome nga gipakita dinhi (asul nga mga laso ug berde nga mga squiggles) nalangkit sa pagporma sa mga bugkos tali sa mga amino acid o uban pang mga monomer. Ang mga tRNA (pula nga mga laso) gipakita nga naghatud sa mga nobela nga monomer (gray nga mga sphere) aron ilakip sa mga polimer. Ang mga molekula sa tubig (pula) ug mga ion (asul) naglibot sa istruktura. Tinubdan: Watson et al, Kinaiyahan Chemistry
Pag-engineer ug bag-ong ribosome
Sa tanang selula, ang mga protina gitigom sa usa ka nanomachine, ang ribosome, nga modawat sa mga instruksiyon gikan sa molekula sa RNA nga gitawag ug messenger RNA (mRNA)—ang mRNA susama sa usa ka nagtrabaho nga kopya sa DNA code sa usa ka gene—ug nagbasa niadtong mga instruksiyon sa pagtigom ug protina, amino acid pinaagi sa amino acid. Katingad-an, ang linear nga kadena sa protina hapit kanunay nga napilo sa usa ka maayo nga pagkahan-ay nga istruktura sa 3D, andam sa pag-alagad sa iyang nabag-o nga katuyoan: ingon usa ka enzyme nga mag-catalyze sa mga reaksyon sa cell, ingon usa ka istruktura nga sangkap sa cell, o ingon usa ka regulator sa ubang mga kalihokan sa cellular. .
Napulo ka tuig na ang milabay, ang pag-retool niining komplikado nga nanomachine daw imposible. Apan ang kalig-on ni Schepartz sa pagduso sa usa ka proyekto aron matuman kini nga katuyoan miresulta sa C-GEM, nga tulo ka tuig sa una nga lima ka tuig nga siklo sa pagpondo.
Usa sa mga tumong sa sentro mao ang paghatag sa ribosome og mga bloke sa pagtukod—gitawag nga monomer—gawas sa mga alpha-amino acid. Aron makab-ot kini nga tumong, ang C-GEM team nagtutok sa mga enzyme nga nagkarga sa mga monomer sa amino acid ngadto sa pagbalhin sa RNA (tRNA), ang mga molekula nga nagdala sa mga amino acid ngadto sa ribosome. Ang matag tRNA gi-barcode aron ipakita kung hain sa 20 ka amino acid ang gidala niini.
Ingon sa gitaho sa a Kinaiyahan Chemistry papel nga gipatik Hunyo 1 ug co-authored sa Schepartz ug graduate mga estudyante Riley Fricke ug Cameron Swenson, ang team nakadiskobre nga ang usa ka pamilya sa tRNA synthetases mahimong load tRNA uban sa upat ka lain-laing mga non-alpha-amino acids. Usa niini mao ang usa ka building block sa nagkalain-laing polyketide therapeutics, lakip ang antibiotics nga erythromycin ug tetracycline.
“Giila namon ang mga enzyme nga nagkarga sa mga tRNA nga adunay mga monomer nga lahi sa istruktura gikan sa bisan unsang butang nga gikarga sa usa ka tRNA kaniadto,” ingon ni Schepartz. “Usa sa mga monomer mao ang usa ka pasiuna nga mahimong gamiton sa pag-assemble sa polyketide-sama nga mga molekula. Ang mga siyentista naningkamot sulod sa mga dekada sa pag-reengineer sa polyketide synthase modules aron makamugna og mga librarya sa natural nga mga produkto. , apan ang bahin sa engineering lisod kaayo.”
Ang mga nobela nga monomer kinabubut-on nga gidawat sa lumad nga ribosome sa bakterya E. colinga nagpakita nga posible nga iapil ang lain-laing mga klase sa kemistriya ngadto sa kasagarang all-amino acid protein polymer.
“Ang pagsukol sa antibiotiko usa ka dako nga problema,” dugang niya. “Kung makatabang kami nga masulbad kana nga problema pinaagi sa pagmugna og mga molekula sa nobela kansang mga gimbuhaton nag-encode sa talagsaon nga mga paagi sa paglihok, kana usa ka dako nga kontribusyon.”
Sa usa ka ikaduhang papel, nga nagpakita sa Mayo 30 sa ACS Central Science, lead author ug postdoctoral nga kauban nga si Chandrima Mujumdar, kauban si Cate ug Schepartz, migamit sa cryogenic electron microscopy (cryo-EM) aron makakuha og detalyadong mga istruktura sa tulo ka may kalabutan nga monomer-walay usa kanila alpha-amino acids-nga gigapos sa E. coli ribosome. Gipakita sa mga detalye kung giunsa kini nga mga monomer nagbugkos – bisan kung labi ka dili maayo kaysa sa mga amino acid – ug naghatag mga pahibalo kung giunsa pag-usab ang mga monomer o ang ribosome aron mapauswag ang katakus sa ribosome nga magamit kini sa paghimo og mga bag-ong polimer.
Sa usa ka ikatulo nga papel, nga nagpakita sa Hunyo 12 sa Kinaiyahan ChemistryCate, Schepartz ug lead author nga si Zoe Watson, usa ka postdoctoral fellow, nagtaho sa cryo-EM structure sa E. coli ribosome samtang nagbugkos sa normal nga alpha-amino acids. Alang niini nga papel, ang team nakigtambayayong sa kompanya nga Schrödinger Inc. sa San Diego, nga naggamit sa mga kompyuter sa pagmodelo sa pagbugkos sa protina. Si Ara Abramyan sa Schrodinger migamit sa cryo-EM structure isip sugod nga punto sa pagpadagan sa metadynamic simulations aron makatabang nga masabtan kung unsa nga dili natural nga mga monomer ang mo-react sa ribosome’s catalytic center—ang peptidyl transferase center (PTC)—ug dili.
Gipasiugda ni Schepartz ug Cate nga kining tanan nga mga tweak sa ribosomal system kinahanglan molihok sa sulod sa usa ka buhi nga selula nga independente sa normal nga mga ribosom aron ang paghimo sa bag-ong mga polimer dili makabalda sa adlaw-adlaw nga produksiyon sa protina nga gikinahanglan alang sa kinabuhi.
“Gusto namon ang mga enzyme-synthetases-ug ribosomes nga magamit sa usa ka cell, tungod kay kana kung giunsa kini nga trabaho mahimong mabag-o,” ingon ni Schepartz. “Kana nga tumong nagkinahanglan og lig-on nga ribosomes, dagkong mga enzyme ug daghang pagsabot mahitungod sa kemistriya kon sa unsang paagi kining komplikadong mga molekular nga makina nagtrabaho. Kini usa ka lisud nga problema, apan daghan nga kalingawan. Ug atong mabutyag ang mga estudyante ug mga postdoc sa pipila ka talagsaon nga siyensiya.”
Dugang impormasyon:
Riley Fricke et al, Pagpalapad sa substrate scope sa pyrrolysyl-transfer RNA synthetase enzymes aron maapil ang non-α-amino acids in vitro ug in vivo, Kinaiyahan Chemistry (2023). DOI: 10.1038/s41557-023-01224-y
Zoe L. Watson et al, Atomistic simulations sa Escherichia coli ribosome naghatag pagpili criteria alang sa translationally aktibo substrates, Kinaiyahan Chemistry (2023). DOI: 10.1038/s41557-023-01226-w
Chandrima Majumdar et al, Aminobenzoic Acid Derivatives Obstruct Induced Fit sa Catalytic Center sa Ribosome, ACS Central Science (2023). DOI: 10.1021/acscentsci.3c00153
Gihatag sa University of California – Berkeley
Citation: Ang pag-retool sa ribosomal translation machine mahimong makapalapad sa kemikal nga repertoire sa mga selula (2023, Hunyo 13) nga nakuha 8 Hulyo 2023 gikan sa https://phys.org/news/2023-06-retooling-ribosomal-machine-chemical-repertoire.html
Kini nga dokumento gipailalom sa copyright. Gawas sa bisan unsang patas nga pakigsabot alang sa katuyoan sa pribadong pagtuon o panukiduki, walay bahin ang mahimong kopyahon nga walay sinulat nga pagtugot. Ang sulud gihatag alang sa katuyoan sa kasayuran lamang.
